
생화학분자생물학회입니다.
유전자 가위의 정확성 측정법 및 증대 방법(Evaluating and Improving Genome-wide Specificity of Programmable Nuclease)
작성자
관리자작성일자
2020-03-23조회수
3358유전자 가위의 정확성 측정법 및 증대 방법
(Evaluating and Improving Genome-wide Specificity of Programmable Nuclease)

김대식
한국생명공학연구원 유전자교정연구센터
dskim89@kribb.re.kr
1. 서론
제3세대 유전자 가위 중 가장 많이 사용되는 Cas9 (CRISPR-associated protein 9) 크리스퍼 유전자 가위는 박테리아의 적응면역체계 (adaptive immune system) 중 하나로 외부 바이러스의 DNA 또는 RNA가 박테리아의 내부로 침입하였을 때 이를 감지하고 잘라서 제거하는 역할을 한다 (1). 2013년 Cas9 크리스퍼 유전자 가위를 이용하여 인간 세포의 유전체 교정이 가능하다는 논문이 보고된 후 다양한 동식물의 유전체 교정에 사용되고 있다. 크리스퍼 유전자 가위는 유전자 교정에 사용되는 인공 효소로써 Cas9 단백질과 gRNA(guide RNA)로 구성된다. Cas9 단백질은 유전체 DNA에서 NGG(N은 A, T, C, G 중 하나)PAM (protospacer adjacent motif) 염기서열을 인식하고 gRNA는 PAM 염기서열 바로 앞에 존재하는 20-bp 염기서열을 인식하게 된다(2). Cas9과 gRNA 복합체가 유전체 DNA에 결합하게 되면 결합 지역에 이중나선손상(double strand break)을 일으키게 된다. 세포 내에서 이중나선손상이 발생하게 되면, 세포는 이를 복구하기 위해 두 가지 수선 체계[비상동재접합(Non-homologous end joining, NHEJ) 또는 상동재조합(Homologous recombination, HR)]를 활성화한다. 비상동재접합은 잘린 DNA를 다시 이어주는 수선 체계이지만 이어주는 과정에서 간혹 몇 개의 염기서열을 삽입(insertion) 또는 결실(deletion)된다(3). 이 과정을 통해 원하는 위치에 변이를 도입할 수 있다. 상동재조합은 비상동재접합과는 달리 세포 내 변이를 유발하지 않는 정교한 방법으로써 세포 내 DNA에서 이중나선손상이 일어났을 경우 유사한 염기서열을 가진 DNA를 주형으로 하여 그 유전정보를 이중나선손상이 발생한 부분으로 이동시키는 것으로써 원하지 않는 염기서열의 삽입 또는 제거가 발생하지 않는다. 상동재조합을 이용하면 원하는 위치에 원하는 서열의 삽입, 결실, 치환(substitution)등을 유도할 수 있다(3).
이처럼 Cas9 크리스퍼 유전자 가위는 질환을 유발할 수 있는 유전변이를 교정하거나 기능이 강화된 세포치료제를 개발하는 도구로써 큰 기대를 모으고 있다. 하지만, Cas9 크리스퍼 유전자 가위가 잘못 작동하여 내가 원하는 위치인 표적 위치 (on-target site)가 아닌 원하지 않는 비표적 위치 (off-target site)를 자를 수 있다는 우려가 제기되었다. Cas9 크리스퍼 유전자 가위는 비표적 위치에 작동하여 그 위치에 변이를 일으킬 수 있을 뿐만 아니라 표적 위치와 비표적 위치를 같은 염색체에서 동시에 자를 경우 두 개의 절단 부위 사이에 있는 부분이 결실되거나 역위 (inversion)가 일어날 수 있으며, 만약 서로 다른 염색체를 자르게 되면 전좌 (translocation)와 같은 염색체 재배열 (chromosomal rearrangement)가 발생할 수 있다(4).

따라서 Cas9 크리스퍼 유전자 가위를 다양한 질병을 치료하는 것에 사용하기 위해서는 비표적 위치에 변이를 일으킬 수 있는 오작동 가능성이 적은 정확성이 뛰어난 유전자 가위를 선택하여 이를 이용하는 것이 중요하다.
2. 유전자 가위의 비표적 위치 검출
인간 유전체 프로젝트(Human Genome Project, HGP)가 2003년 총 13년 동안 27억 달러가 소요되어 완성된 이후 차세대 염기서열 분석방법 (Next Generation Sequencing, NGS)은 비약적으로 발전하여, 2020년 현재는 한 사람의 염색체 DNA를 전유전체시퀀싱 (Whole genome sequencing, WGS)을 진행하는데 2-4주 정도 걸리며 비용은 2000달러 미만이 소요된다.
차세대 염기서열 분석방법의 발전은 유전자 가위를 이용한 유전자 교정 분야를 한단계 끌어올렸다. 예를 들면, 유전자 가위가 개발된 초기에는 T7E1 (T7 Endonuclease I) 이나 Surveyor nuclease와 같은 mismatch-specific endonucleases를 이용하여 유전자 가위에 의한 유전자 교정 비율을 간접적으로 확인하였으나 차세대 염기서열 분석 방법이 발전하면서 변이가 일어난 부분을 PCR을 통해 증폭시키고 증폭된 서열을 NGS를 통해 개별적으로 읽음으로써 염기서열의 정확한 변이 비율과 변이 종류에 대해 손쉽게 알 수 있게 되었다.
유전자가위의 비표적 위치를 찾기 위해 연구자들이 처음 진행한 방법은 유전체에서 PAM 염기서열을 가지고 있으면서 표적 위치의 서열과 유사한 서열을 찾고 그 위치에 변이가 발생하는지 여부를 확인하는 것이었다(5). 하지만 이러한 방법으로는 전유전체에서 bias가 없이 비표적 위치를 찾을 수 없었기 때문에 절단유전체시퀀싱 (Digenome-seq) 방법을 고안하였다(6).
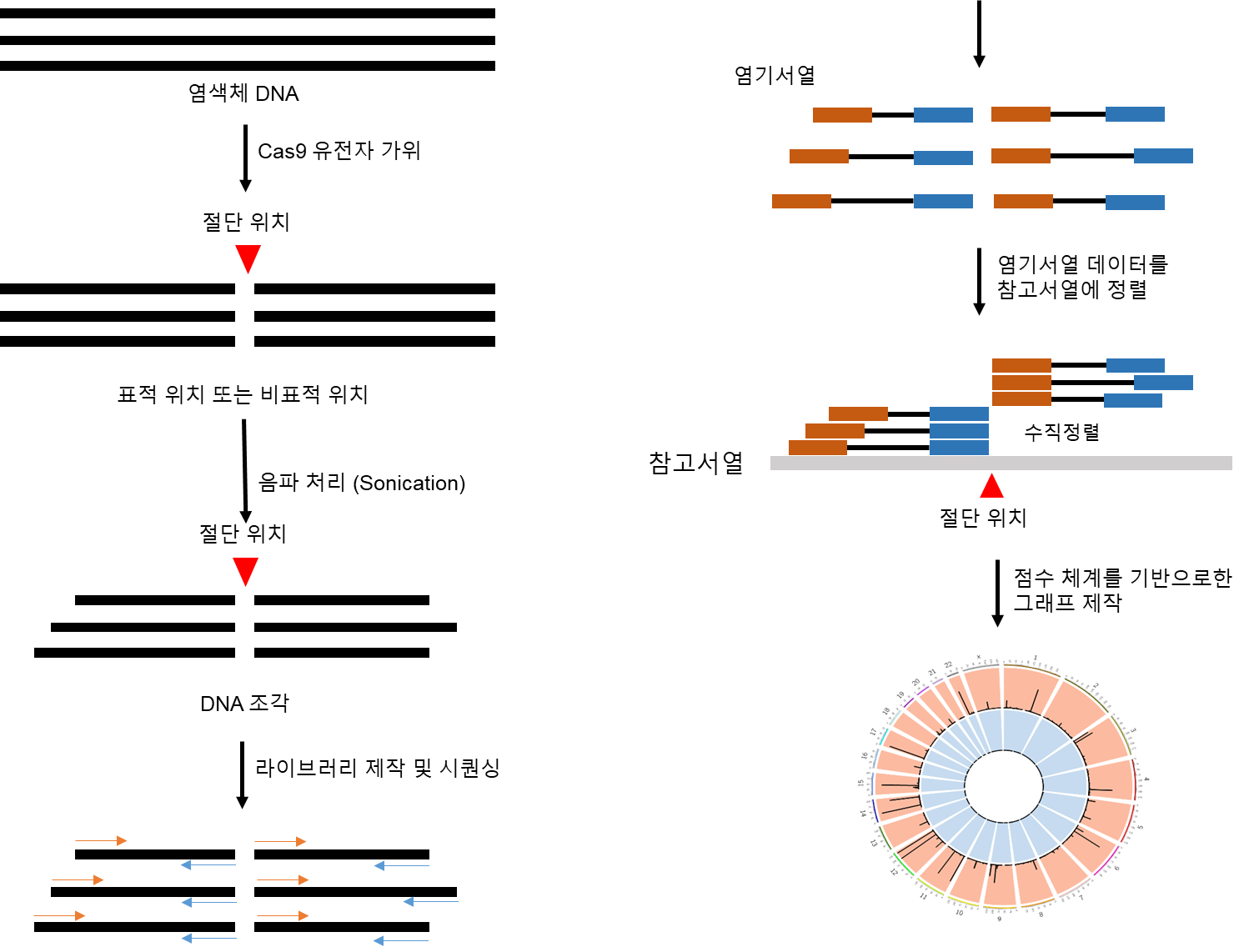
정제된 Cas9 단백질과 in vitro에서 전사(transcription)된 gRNA를 섞어 Cas9 RNP (ribonucleoprotein) 복합체를 만든 후 이를 세포에서 추출한 염색체 DNA (genomic DNA)와 함께 incubation 시켜준다 (그림 2). 그러면 Cas9과 gRNA 복합체는 염색체 DNA의 표적 위치와 비표적 위치에 이중나선손상을 유도한다. Cas9 RNP에 의해 표적 위치와 비표적 위치가 절단된 염색체 DNA를 이용하여 fragmentation, end repair, A-tailing, adaptor ligation 과정을 거쳐 시퀀싱을 위한 DNA library를 제작하고, 만들어진 DNA library를 이용하여 전유전체시퀀싱을 진행하였다 (그림 2).
전유전체시퀀싱 과정을 통해 얻은 염기서열 데이터 (sequencing reads)를 참조 염기서열 (reference genome; 생물의 종을 대표하는 유전체 염기서열)에 정렬 (alignment/mapping) 하였다. 표적 위치에서 정렬된 염기서열 데이터를 보면 세포에서 추출한 염색체 DNA를 아무 처리 없이 전유전체시퀀싱을 하였을 경우에는 염기서열 데이터들이 아무 규칙 없이 참조 염기서열에 정렬되는 staggered alignments 형태를 보이게 된다. 하지만 Cas9 RNP를 처리하여 표적위치에 이중나선손상을 일으킨 후 전유전체시퀀싱을 하였을 경우에는 절단된 위치를 중심으로 straight alignments 형태를 보여주는 것을 확인할 수 있다 (그림 2). 이러한 결과를 기반으로 Cas9 RNP에 의해 절단됨으로써 staggered alignments가 있는 염색체 위치에는 높은 값을 주고 straight alignments가 있는 위치에는 낮은 값을 주는 점수체계 (scoring system)를 만들었다. 점수체계를 기반으로 유전자 가위의 비표적 위치를 전유전체에서 찾을 수 있다 (그림 2). 이러한 과정은 생명정보학 (bioinformatics)를 전혀 알지 못해도 진행 가능하도록 web 버전으로 구현하였다(7).
3. 유전자 가위의 정확성 증대
Cas9 크리스퍼 유전자 가위가 비표적 위치에도 변이를 일으킨다는 사실이 보고된 이후로 많은 연구자들이 유전자 가위의 정확성을 증대시키기 위해 노력하였다. 먼저 연구자들은 gRNA 길이를 조절하였을 때 Cas9 크리스퍼 유전자 가위의 정확성이 어떻게 변화하는지 확인하였다. 그 결과 타겟 DNA의 20bp를 인식하는 gRNA 대신 인식하는 DNA가 짧은 gRNA (17-18bp)를 사용하였을 때 정확도가 증가하였으며, 마찬가지로 gRNA의 5’ 끝에 두개의 구아닌(G) 염기를 더해준 긴 gRNA를 사용하였을 때도 마찬가지로 정확도가 증가하는 것을 확인할 수 있었다 (그림 3)(4).
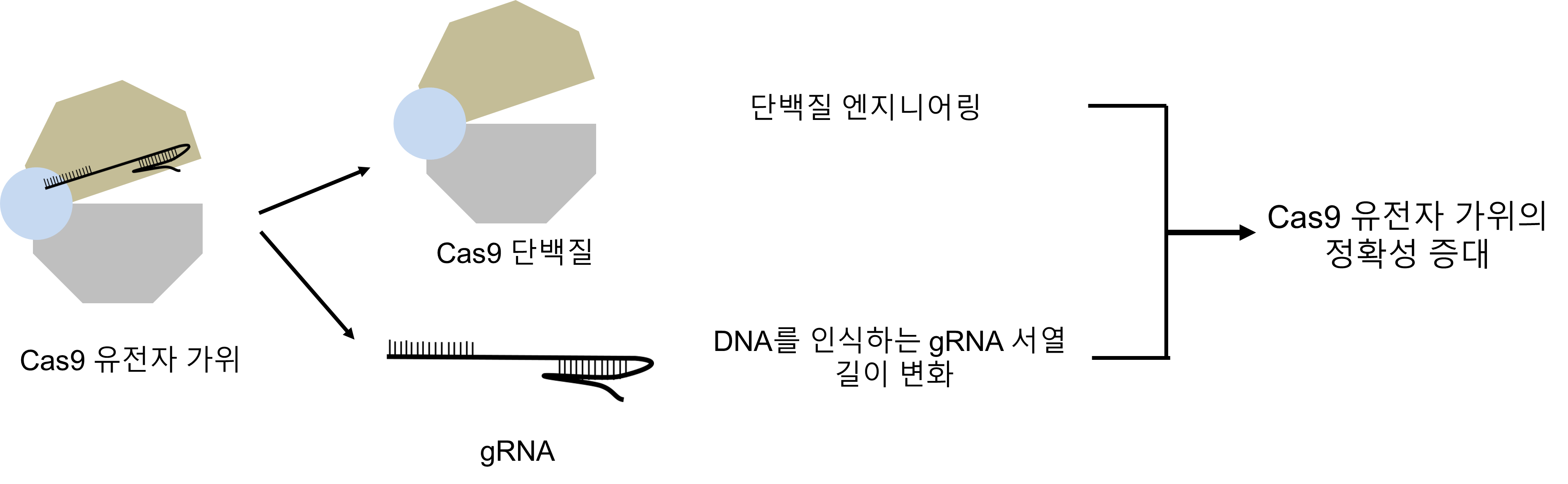
일반적으로 유전자 가위를 세포 내에 전달할 때 Cas9 단백질과 gRNA를 발현하는 plasmid DNA를 세포 내로 전달해준다. 새포 내로 전달된 plasmid DNA는 3일 이상의 긴 시간 동안 Cas9 단백질을 발현시킨다. 장기간 Cas9에 의해 노출되면 비표적 위치의 유전자 변이가 커질 수 있기 때문에 plasmid DNA 전달 방법을 Cas9 단백질과 gRNA를 모두 in vitro에서 합성하여 이를 복합체로 만든 후 세포 내로 전달하는 Cas9 RNP 전달 방법으로 바꾼 후 정확성을 측정하였다. 그 결과 표적 위치에서의 변이 비율은 plasmid DNA 전달 방법과 RNP 전달 방법이 큰 차이가 없지만 비표적 위치에서의 변이 비율은 plasmid DNA 전달 방법에 비해 RNP 전달 방법이 훨씬 낮은 것을 확인할 수 있었다(8).
마지막으로 Cas9 크리스퍼 유전자 가위의 정확성을 높이기 위해 Cas9 단백질을 엔지니어링 하는 방법을 사용하였다. 가장 먼저 진행된 일은 Cas9의 3차 구조를 기반으로 gRNA와 타겟 DNA가 결합하는 부분 또는 gRNA와 결합하지 않은 타겟 DNA 부분과 강하게 결합하고 있는 Cas9의 아미노산 (amino acid) 부분을 약화시키는 rational design 방법을 사용하였다. 이러한 방법을 사용하여 만든 Cas9 variant에는 eCas9, Cas9-HF, HypaCas9 등이 있다. 이를 이용하면 표적 위치에서는 Cas9 크리스퍼 유전자 가위와 DNA의 결합 강도가 강하기 때문에 변이가 없는 Cas9 크리스퍼 유전자 가위와 결합력이 약화된 Cas9 크리스퍼 유전자 가위가 유사한 정도의 변이를 일으키지만 비표적 위치에서는 Cas9 크리스퍼 유전자 가위와 DNA의 결합 강도가 낮기 때문에 변이가 없는 Cas9의 경우 약한 결합에 따른 변이가 발생하지만 약화된 Cas9 크리스퍼 유전자 가위는 DNA와 거의 결합하지 못하면서 비표적 위치에서의 변이를 일으키지 못한다. 결과적으로 표적 위치에는 변이를 일으키지만 비표적 위치에서는 변이를 일으키지 못하므로 정확도를 증대시킬 수 있다. 다른 방법으로는 directed evolution 방법을 이용하여 정확도를 높이는 것이다. Cas9 크리스퍼 유전자 가위에 변이를 무작위로 넣어준 후 표적 위치는 자르고 비표적 위치를 자르지 못하는 변이를 찾는 방법으로써 이를 이용하여 만든 Cas9 variant는 EvoCas9과 SniperCas9이 있다 (그림 3)(4).
4. 결론
2013년 Cas9 크리스퍼 유전자 가위를 이용하여 사람 세포에서 유전자 변이를 일으킬 수 있다는 논문이 처음 나온 후 빠르게 발전하고 있다. 예를 들면 Cas9과는 전혀 다른 PAM 서열과 절단 종류를 가지고 있는 Cpf1이 사람 세포에서 사용할 수 있도록 개발되었으며, 유전자를 자르지 않고 타겟 위치에 있는 시토신(C) 또는 아데닌(A)을 각각 티민(T) 또는 구아닌(G)으로 바꿀 수 있는 염기 교정 유전자 가위가 개발되었다. 최근에는 원하는 위치에 삽입, 절단, 치환이 가능한 프라임에디터 (prime editor)가 개발되면서 유전자 가위 분야에 발달도 가속화되고 있다.
유전자 가위의 발달과 더불어 이를 이용하여 치료에 사용하고자 하는 시도가 많이 이루어지고 있다. 에이즈를 치료하기 위해 에이즈 환자 T 세포에 유전자 가위를 이용하여 CCR5 유전자를 제거한 후 CCR5가 제거된 세포를 다시 몸에 주입하는 ex vivo 방법이 임상시험이 진행 중이며, 최근에는 ‘CEP290 (Centrosomal Protein 290)’라는 유전자에 결함이 생김으로써 앞이 보이지 않는 질환을 가진 환자의 눈에 직접적으로 유전자 가위를 넣는 임상시험이 진행되었다.
이처럼 유전자 가위를 이용하여 질환을 치료하고자 하는 시도는 점점 많아 질 것이며, 검사를 통해 부작용을 예측하고 이를 최소화하는 것이 중요하다. 질환을 치료하기 위한 약물을 사용할 때 이에 대한 부작용을 정확히 파악해야 부작용을 완화할 수 있는 약물을 개발할 수 있다. 이처럼 유전자 가위의 비표적 위치를 정확히 파악해야 이를 대비를 하는 것이 가능하다. 따라서 유전자 가위의 비표적 위치를 전유전체에서 편향없이 측정하는 방법을 개발하고 발전시키는 연구가 필요하다. 마지막으로 Digenome-seq을 통한 유전자 가위의 정확성 측정이 이를 치료제로써 사용 할 때 안정성을 평가하기 위한 중요한 요소로 이용될 것으로 기대한다.
참고문헌
1.
|
Wiedenheft B, Sternberg SH and Doudna JA (2012) RNA-guided genetic silencing systems in bacteria and archaea. Nature 482, 331-338 |
2.
|
Jinek M, Chylinski K, Fonfara I, Hauer M, Doudna JA and Charpentier E (2012) A programmable dual-RNA-guided DNA endonuclease in adaptive bacterial immunity. Science 337, 816-821 |
3. |
Kim H and Kim JS (2014) A guide to genome engineering with programmable nucleases. Nat Rev Genet 15, 321-334 |
4.
|
Kim D, Luk K, Wolfe SA and Kim JS (2019) Evaluating and Enhancing Target Specificity of Gene-Editing Nucleases and Deaminases. Annu Rev Biochem 88, 191-220 |
5.
|
Cho SW, Kim S, Kim Y et al (2014) Analysis of off-target effects of CRISPR/Cas-derived RNA-guided endonucleases and nickases. Genome Res 24, 132-141 |
6.
|
Kim D, Bae S, Park J et al (2015) Digenome-seq: genome-wide profiling of CRISPR-Cas9 off-target effects in human cells. Nat Methods 12, 237-243 |
7. |
Park J, Childs L, Kim D et al (2017) Digenome-seq web tool for profiling CRISPR specificity. Nat Methods 14, 548-549 |
8.
|
Kim S, Kim D, Cho SW, Kim J and Kim JS (2014) Highly efficient RNA-guided genome editing in human cells via delivery of purified Cas9 ribonucleoproteins. Genome Res 24, 1012-1019 |
첨부파일